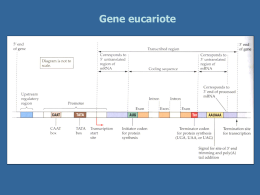
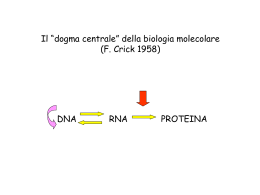
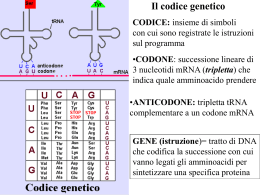
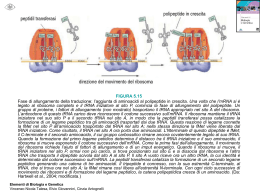
TRADUZIONE LA TRADUZIONE E’ QUEL PROCESSO ATTRAVERSO CUI SI PASSA DAL LINGUAGGIO RIBONUCLEOTIDICO DELL’RNA A QUELLO AMINOACIDICO DELLE PROTEINE. IL CODICE GENETICO E’ L’INSIEME DI CODONI (TRIPLETTE NUCLEOTIDICHE) A CUI CORRISPONDONO I VARI AMINOACIDI PIU’ I CODONI DI TERMINE (CODONI NON SENSO). SUE PROPRIETA’ FONDAMENTALI SONO: i) CONTINUITA’ (Eccezione di alcuni fagi –es es.: .: fX174 X174- in cui il codice è embricato); ii) DEGENERAZIONE DEGENERAZIONE;; iii) UNIVERSALITA’ UNIVERSALITA’ (Ad eccezione di alcuni codoni mitocondriali cha hanno un significato diverso rispetto agli mRNA citoplasmatici) ESPERIMENTO DI BRENNER E CRICK: L’UNITA’ ELEMENTARE CODIFICANTE E’ UNA TRIPLETTA! ABC ABC ABC ABC ABC… i) 1° delezione (B della 1° 1° tripletta) – ACA BCA BCA BCA BC… ii) 2° delezione (C della 2° 2° tripletta) – ACA BAB CAB CAB C… iii) 3° delezione (A della 4° 4° tripletta) – ACA BAB CBC ABC… DOPO LA TERZA MUTAZIONE (DELEZIONE IN QUESTO CASO) RIAPPARE LA TRIPLETTA ABC, SI RIPRISTINA LA CORRETTA CORNICE DI LETTURA ESPERIMENTI DI NIREMBERG, LEDER E KHORANA: LA DECIFRA= ZIONE DEL CODICE SAGGIO DI LEGAME AI RIBOSOMI: SE L’AMMINOACIL-tRNA RICONOSCE LA TRIPLETTA, VI SI LEGA E NON RIESCE A PASSARE IL FILTRO CHE, COSì, DIVIENE RADIOATTIVO. IL CODICE GENETICO (Khorana (Khorana;; Ochoa Ochoa;; Niremberg Niremberg;; Matthaei;; Leder) Matthaei I CODONI 5’5’-UGA UGA--3’ E 5’5’-UAG UAG--3’ OLTRE AD ESSERE NON SENSO, POSSONO CODIFICARE PER SELENOCISTEINA E PIRROLISINA PIRROLISINA,, RISPETTIVAMENTE. 61 CODONI CODIFICANTI PER 20 aa aa.. 3 SEGNALI DI STOP I RIBOSOMI I Ribosomi hanno un diametro di circa 1515 -30 nm (Procarioti ed Eucarioti Eucarioti,, rispettivamente), sono costituiti da proteine ed rRNA rRNA.. Sia nei Procarioti che negli Eucarioti Eucarioti,, sono costituiti da una subunità maggiore e da una subunità minore minore.. PROCARIOTI SUBUNITA’ MAGGIORE = 50S (rRNA 23S e 5S + 34 proteine) SUBUNITA’ MINORE = 30S (rRNA 16S + 21 proteine) 70S SUBUNITA’ MAGGIORE = 60S (rRNA 28S, 5.8S e 5S + 45 proteine) EUCARIOTI SUBUNITA’ MINORE = 40S (rRNA 18S + 33 proteine) 80S I RIBOSOMI EUCARIOTICI POSSONO ARRIVARE AD ESSERE CENTINAIA DI MIGLIAIA IN UNA CELLULA IN ATTIVA SINTESI PROTEICA. SI POSSONO TROVARE: 1) LIBERI NEL CITOPLASMA (SINTETIZZANO PROTEINE CHE RIMARRANNO ALL’INTERNO DEL CITOSOL); 2) ADERENTI ALLE MEMBRANE DEL RER (RETICOLO ENDOPLA= SMATICO RUVIDO) O DEL NUCLEO (SINTETIZZANO PROTEINE CHE VERRANNO SECRETE DALLA CELLULA O CHE RIMARRANNO RACCHIUSE IN VESCICOLE ALL’INTERNO DEL CITOPLASMA CELLULARE) MATURAZIONE DEGLI rRNA EUCARIOTICI tRNA Assumono una conformazione secondo il modello a trifoglio Le differenze nelle sequenze nucleotidiche determinano la capacità di legare un amminoacido specifico L’ansa II contiene la sequenza di 3 nucleotidi detta ANTICODONE che si appaia, durante la traduzione al codone dell’mRNA dell’ mRNA Questo appaiamento è fondamentale per l’inserimento dell’amminoacido corretto,come specificato dall’ m-RNA RNA,, nella catena polipeptidica in crescita. STRUTTURA DELL’ mRNA MATURO Cap 5’ 7mGppp initiation 5’ untranslated region AUG translated region UGA 3’ untranslated region termination polyadenylation signal AAUAAA (A)~200 poly(A) tail 3’ NOTA: DISPOSIZIONE ANTIPARALLELA TRA CODONE NOTA: DELL’mRNA DELL’ mRNA ED ANTICODONE DEL tRNA Attivazione dell’aminoacido (Fase ATP ATP-dipendente dipendente)) ATP + Aminoacido = Aminoacido adenilato + 2P Aminoacido adenilato + tRNA = AminoaciltRNA + AMP Azione dell’ dell’aminoacil aminoaciltRNA -sintetasi Anidride acida (legame ad alta energia acilacil -fosfato fosfato)) AminoacilAminoacil -tRNA TRADUZIONE NEI PROCARIOTI Fase GTP GTP-dipendente Inizio Sequenza di Shine ShineDalgarno:: facilita il Dalgarno riconoscimento dell’mRNA dell’mRNA da parte della subunità minore del Ribosoma. Ribosoma. In particolare la sequenza consenso 5’ 5’-AGGAGGU AGGAGGU-3’ dell’mRNA (che si trova in prossimità della tripletta di inizio AUG) complementarizza con la sequenza 3’ 3’-UCCUCCA UCCUCCA-5’ dell’rRNA 16S (subunità (subunità minore del ribosoma ribosoma)! )! Fase GTP GTP-dipendente Inizio IF1 ED IF3 HANNO IL COMPITO DI STABILIZZARE LA SUBUNITA’ MINORE DEL RIBOSOMA CHE, COSì TENDERà A NON LEGARSI CON LA SUBUNITà MAGGIORE. IF2,, GRAZIE ALL’IDROLISI DI GTP, PORTA IL PRIMO aa IF2 aa.. (f (f-Met Met)) SPECIFICATO DA AUG. fMet:: il primo fMet aa.. ad essere aa incorporato nella catena aa.. nascente aa Fase GTP GTP-dipendente Inizio Assemblaggio del Ribosoma Fase GTP GTP-dipendente Inizio (Assemblaggio del Ribosoma) SITO P (PEPTIDICO) = Vi si trova legato il f-Met Met-tRNA SITO A (AMINOACIDICO) = Accoglie l’aa l’aa.. Successivo che si legherà ad f-Met SITO E (USCITA) Fase GTP GTP-dipendente Inizio…Ricapitolando 1. Il tRNA iniziatore portante la formil formil-metionina si lega alla subunità minore del ribosoma assieme a dei fattori d’inizio (IF1, IF2 ed IF3). 2. Si lega l’mRNA l’mRNA,, la subunità minore del ribosoma scorre sull’mRNA sull’mRNA fino a quando non incontra il codone d’inizio AUG. 3. Si instaura il legame tra l’AUG e l’anticodone del tRNA iniziatore. 4. Si associa la subunità maggiore. 5. Il tRNA iniziatore occupa il sito P, al sito A è presente il secondo codone dell’ mRNA Procarioti: 20 aa al secondo Eucarioti:: 2 aa al secondo Eucarioti Fase GTP GTP-dipendente Allungamento ALLUNGAMENTO MEDIATO DAI FATTORI EF EF--Ts Ts--Tu ed EFG. Tu SI DISSOCIA DA Ts E, UTILIZZANDO GTP, PORTA L’AMINOACIL L’ AMINOACIL--tRNA SUL MESSAGGERO. DOPO AVER LIBERATO L’AA. Tu SI RICONGIUNGE A Ts…IL CICLO RIPRENDE PER LA TRIPLETTA SUCCESSIVA. Fase GTP GTP-dipendente Allungamento Formazione del legame peptidico mediante reazione di transpeptidazione transpeptidazione.. NOTA: Il legame Si forma sfruttando l’energia contenuta nel legame estere tra tRNA ed aa aa.. (formatosi durante l’attivazione dell’aa dell’aa.)!!! .)!!! Formazione del legame peptidico L’attività catalitica peptidiltransferasica è contenuta nella subunità maggiore del ribosoma (rRNA (rRNA 23S) Fase GTP GTP-dipendente Allungamento Al sito A si lega il tRNA acilato (portante il secondo aminoacido della catena polipeptidica polipeptidica). ). Si forma il legame peptidico tra l’estremità COOH terminale della Metionina e l’estremità NH2 terminale del secondo aminoacido ad opera dell’attività enzimatica della subunità maggiore del ribosoma. L’energia necessaria è data dall’attivazione aminoacidica.. aminoacidica TRASLOCAZIONE Il tRNA scarico che occupava il sito P occuperà il sito E il tRNA portante il dipeptide che occupava il sito A occuperà il sito P al sito A sarà presente il terzo codone dell’mRNA dell’mRNA pronto ad ospitare un nuovo tRNA acilato Fase GTP GTP-dipendente Terminazione La presenza di più segnali di STOP stimola la comparsa di fattori di rilascio RF1 RF1,, RF2 ed RF3 RF3.. Quando al sito A sarà presente uno dei 3 segnali di arresto (UAA, UGA, UAG), si legheranno dei fattori di terminazione e la sintesi sarà bloccata I fattori di rilascio si legano a qualunque ribosoma col segnale di stop nel sito A, forzando la peptidil transferasi a ad aggiungere una molecola di acqua invece di un aminoacido al peptidil tRNA tRNA.. Questo libera l’estremità carbossilica della Il fattore RRF favorisce catena polipepptidica polipepptidica.. il disassemblaggio Vi sono due classi di fattori di rilascio. I delle due subunità fattori di classe I riconoscono i segnali di stop e innescano l’idrolisi della catena polipeptidica.. I fattori di classe II (regolati polipeptidica da GTP) stimolano la dissociazione dei fattori di classe I dal ribosoma. I fattori di rilascio di classe I simulano un tRNA dal punto di vista strutturale possedendo un peptide anticodone (SPF) che riconosce il segnale di stop ed un motivo GGQ, vicino al sito peptidiltransferasico che stimola l’idrolisi del peptide. ribosomali!! ribosomali I ribosomi scorrono numerosi l’uno dietro l’altro, sull’mRNA sull’mRNA formando i POLISOMI, al fine di sfruttare numerose volte la stessa molecola di mRNA che ha una emivita di poche ore! Traduzione - Inizio fMet Large subunit 5’ E P A 3’ UAC GAG...CU-AUG--UUC--CUU--AGU--GGU--AGA--GCU--GUA--UGA-AT GCA...TAAAAAA Small mRNA subunit Traduzione - Allungamento Polypeptide Arg Met Phe Leu Ser Aminoacyl tRNA Gly Ribosome P A E 3’ CCA GAG...CU-AUG--UUC--CUU--AGU--GGU--AGA--GCU--GUA--UGA-AT GCA...TAAAAAA 5’ mRNA Traduzione - Allungamento Polypeptide Met Phe Leu Ser Gly Arg Aminoacyl tRNA Ribosome 5’ E P A 3’ CCA UCU GAG...CU-AUG--UUC--CUU--AGU--GGU--AGA--GCU--GUA--UGA-AT GCA...TAAAAAA mRNA Traduzione - Allungamento Polypeptide Met Phe Leu Ser Gly Arg Ribosome E P A CCA UCU GAG...CU-AUG--UUC--CUU--AGU--GGU--AGA--GCU--GUA--UGA-AT GCA...TAAAAAA 5’ mRNA 3’ Traduzione - Allungamento Polypeptide Met Phe Leu Ala Ser Gly Aminoacyl tRNA Arg Ribosome P E CCA 5’ A 3’ UCU GAG...CU-AUG--UUC--CUU--AGU--GGU--AGA--GCU--GUA--UGA-AT GCA...TAAAAAA mRNA Traduzione - Allungamento Polypeptide Met Phe Leu Ser Gly Arg Ribosome 5’ E Ala P A 3’ UCU CGA GAG...CU-AUG--UUC--CUU--AGU--GGU--AGA--GCU--GUA--UGA-AT GCA...TAAAAAA mRNA TRADUZIONE NEGLI EUCARIOTI PRINCIPALI DIFFERENZE CON I PROCARIOTI 1) Fase di inizio regolata da una decina di fattori 2) Aminoacido iniziatore è la Met (e non la f-Met Met). ). Esistono due MetMet -tRNA diversi: uno che riconosce il codone di inizio e l’altro che riconosce i codoni successivi 3) Non c’è una Sequenza Shine Shine-Dalgarno Dalgarno:: la subunità minore del ribosoma dopo aver riconosciuto il 5’cap 5’cap,, inizia uno scanning della molecola di mRNA fino ad incontrare (dopo in media 100 nt. Dall’inizio) l’AUG 4) Mancando la sequenza Shine Shine-Dalgarno Dalgarno,, a livello degli mRNA eucariotici l’AUG viene individuato poiché all’interno di una sequenza (GCCGCCA/G CCAUG CC AUGG) G) detta di Kozak 5) Gli mRNA eucariotici sono detti monocistronici 6) I Fattori di rilascio sono 3 nei Procarioti contro 1 (eRF3) degli Eucarioti NOTA: La conoscenza approfondita delle differenze dei processi molecolari NOTA: coinvolti nella traduzione propro- ed eucariotica ha portato alla produzione di molecole antibiotiche quanto più selettive possibile e pertanto meno tossiche per le cellule eucariotiche eucariotiche!! (Es (Es:: Antibiotici Eritromicina e Streptomicina) QUESTO MECCANISMO RENDE PIU’ EFFICIENTE LA TRADUZIONE ED AVVIENE SOPRATTUTTO IN MITOSI, DOPO LA METAFASE! Il Genoma cellulare specifica inoltre: • La struttura primaria delle proteine • Destinazione delle proteine all’interno della cellula • Presenza o assenza della proteina in un determinato tipo cellulare o in un determinato momento della vita cellulare • La struttura primaria di RNA non tradotti Modificazioni post post-traduzionali • Glicosilazione • Acetilazione • Fosforilazione
Scarica