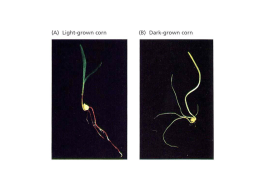
Il ruolo della luce nello sviluppo Giorno Notte Luce Buio seme plantula pianta adulta La luce rappresenta il fattore ambientale più importante nella vita delle piante. Le piante, infatti, sentono e rispondono a: • • • • La presenza/assenza di luce la lunghezza d’onda e l’intensità (fluence rate) L’orientamento la durata giorno/notte (ciclo circadiano) La luce, infatti: • regola molti aspetti dello sviluppo /differenziamento: – fotomorfogenesi v/s skotomorfogenesi – – – – – germinazione dei semi allungamento dell’ipocotile fioritura ritmo circadiano risposte trofiche (fototropismo) La risposta di “de-eziolamento” è stata molto studiata come modello per la comprensione dei meccanismi coinvolti nella percezione della luce, nella trasduzione del segnale, e nella regolazione trascrizionale, per la semplicità del sistema e dello screening genetico. skotomorfogenesi plantula cresciuta al buio fotomorfogenesi plantula creciuta alla luce Blu/UV RED/FAR RED La percezione della luce avviene attraverso 3 classi di fotorecettori, che agiscono in modo indipendente e cooperativo: • FOTOTROPINE (Phot 1 e 2 in Arabidopsis) • CRIPTOCROMI (Cry 1, 2, 3 in Arabidopsis) • FITOCROMI (PhyA,B,C,D,E ) • R UV-B (caratterizzati mediante spettroscopia) Light Parameters F Red Red Transduction Pathway Light-regulated Photomorphogenic display genes Photorecep. components phyA phyB HY5 CAB COP1 RBCS COP9 Blue Phot/Cry DET1 FUS UV-A Phot/Cry UV-B UV-B receptor Seed germination PHYA Seedling De-etiolation PAL Phototropism CHS Shade avoidance etc Floral Induction Trattamenti con intensità diverse di luce HIR > 1000 mol/m2 LFR 1-1000 mol/m2 (fotoreversibilità) VLFR 0.1 mol/m2 Funzioni membri della famiglia del Fitocromo durante lo sviluppo Fitocromo Fotorecezione Attività fisiologiche primarie phyA VLFRs HIRs Germinazione semi (UV,visibile,FR) deeziolamento plantule (FRc), induzione fioritura in LD phyB LFRs R-HIRs Germinazione semi (Rc) deeziolamento plantule (Rc) phyC R-HIRs deeziolamento plantule (Rc) phyD EOD-FR risposta di fuga dall’ombra (allungamento internodi, fioritura) phyE LFRs EOD-FR Germinazione semi risposta di fuga dall’ombra (allungamento internodi, fioritura) I Fitocromi I Fitocromi sono codificati da una famiglia multigenica: • in Arabidopsis 5 geni, PHYA-PHYE • I 5 fitocromi sono tutti espressi in modo ubiquitario • il fitocromo purificato è in forma di omodimero di 125kD • il fitocromo attivo è presente come omodimero • ogni polipeptide lega un cromoforo tetrapirrolico, fitocromobilina, con un legame tioetere, su una cisteina conservata • i 5 fitocromi legano lo stesso cromoforo • la regione C-ter media la dimerizzazione Struttura di una molecola di Fitocromo 1) Albero filogenetico dei cinque geni Phy AtPhyA AtPhyB AtPhyC AtPhyD AtPhyE 80% identità aacidica 2) Struttura proteica dei fitocromi N terminale C terminale F D1 F P1 P2 D2 HKRD = fluorocromo D1, D2 = dominio di dimerizzazione P1, P2 = dominio PAS (interazione proteina-proteina HKRD = dominio istidina-chinasico 1210 aa Omologie strutturali/funzionali tra Phy batterici e vegetali chromophore PSD HKD BATTERI chromophore PSD PRD PSD:photosensory domain con cromoforo HKD:dominio istidina chinasi PRD:dominio PAS-related HKRD:dominio istidina chinasi-related HKRD PIANTE La funzione dei fitocromi è basata sulla capacità di interconversione reversibile tra la forma Pr e quella Pfr: •La forma Pr, biologicamente inattiva, assorbe luce rossa (R) •La forma Pfr, biologicamente attiva, assorbe luce rosso lontano (FR) •La percezione del segnale luminoso è seguita da un cambio conformazionale •La percezione del segnale luminoso attiva poi vie di trasduzione del segnale I fitocromi si dividono in 2 classi: • tipo I, instabile alla luce (phyA) • tipo II, stabile alla luce (phyB-E) I fitocromi quindi fungono da sensori del rapporto R/FR nell’ambiente: •normalmente R/FR ~ 1.2 •le strutture fotosintetiche assorbono R, indi il rapporto diminuisce •Il rapporto R/FR è indicativo anche della “densità di popolazione” Attività del fitocromo •Attività chinasica luce-regolata: -Autofosforilazione (ser/thr chinasi) -Legame con PKS1 (PhytocromeKinaseSubstrate) nel citoplasma -Legame con diversi TF (PIF3, HY5, COP1) nel nucleo Ser-rich N-Ter Extension NTE Fosforilata in Pr e Pfr in vivo Fosforilata in Pfr in vivo Localizzazione del fitocromo •Citoplasmica: -“Phy sono molecole solubili, citoplasmatiche…” -Esperimenti di microiniezioni con a/antagonisti 2°messaggeri noti -Localizzazione immunocitochimica •Nucleare: -Analisi istologica di proteine chimeriche PhY-GFP, PhyGUS, biologicamente attive (complementazione di mutanti phy) -Legame di PhyB/PhyA con TF luce-regolati (PIF3) di Red light B B B B* B Pr B B Pfr B* 35S:PhyB::GFP * B 630X B* Activated 35S:PhyB::GFP PhyB-GFP localization in seeds WT phyB::GFP B* B*
Scarica